RIBOSOME DISPLAY
140 likes | 348 Views
RIBOSOME DISPLAY. Ania Grochot. Dlaczego inne metody są gorsze?. hybrydomy Białko musi być immunogenne ale nie może być letalne Otrzymane przeciwciała są pochodzenia zwierzęcego Faktyczne powinowactwo przeciwciał produkowanych in vivo nie przekracza 10 10 M -1

RIBOSOME DISPLAY
E N D
Presentation Transcript
RIBOSOME DISPLAY Ania Grochot
Dlaczego inne metody są gorsze? hybrydomy • Białko musi być immunogenne ale nie może być letalne • Otrzymane przeciwciała są pochodzenia zwierzęcego • Faktyczne powinowactwo przeciwciał produkowanych in vivo nie przekracza 1010 M-1 (wyższe powinowactwo nie jest korzystne) • Metoda czaso- i pracochłonna Foote, Eisen Proc. Natl. Acad. Sci. U.S.A. 92, 1254
Dlaczego inne metody są gorsze? Phage display • Limit transfekcji– wielkość biblioteki 1010 • Białko nie może być toksyczne dla bakterii • Trudność elucji fagów niosących przeciwciała z wysokim powinowactwem • Wprowadzanie każdej mutacji w genie kodującym przeciwciało wiąże się z rozpoczęciem pracy od początku • Metoda czaso- i pracochłonna
Okazuje się, że: • Istnieje możliwość kotranslacyjnego zwijania białka in vitro • Uwolnienie z rybosomu nie jest konieczne do prawidłowego zwijania białka • Białko związane do rybosomu może wykazywać aktywność biologiczną Schaffitzel, Hanes Journal of immun. methods 231, 119-135
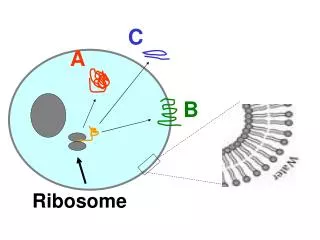
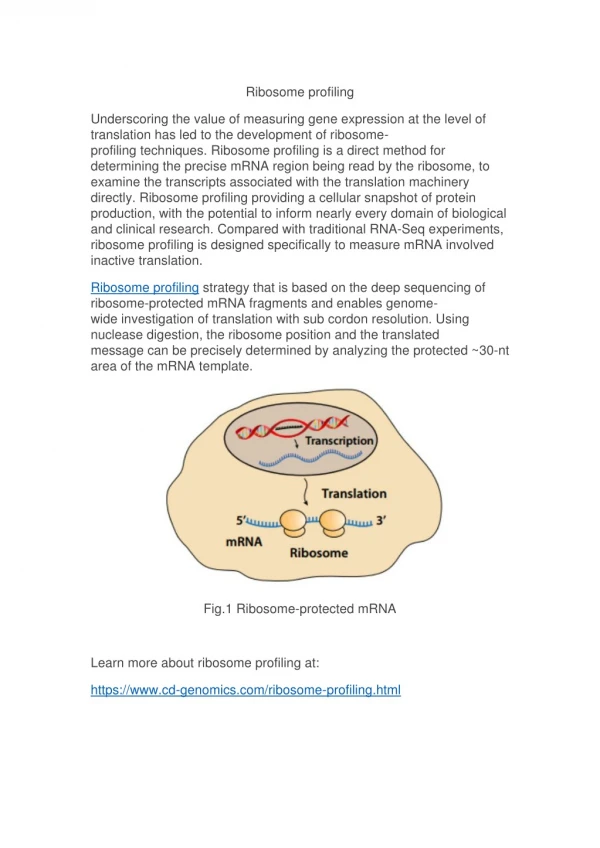
RD? Co to takiego? Ribosome display to pierwsza metoda screeningu bibliotek (np. HuCAL) i otrzymywania funkcjonalnych białek, prowadzona w całości in vitro;powstające białko jest aktywne, jednocześnie pozostając przyczepionym do kompleksu rybosomu i mRNA.
mRNA In vitro transkrypcja DNA In vitro translacja Ekstrakt S30 E.coli lub z retikulocytów królika RT PCR 5’ 3’ 5’ 3’ Izolacja mRNA Selekcja 5’ 3’ 3’ 5’ dysocjacja
Skąd wziąć DNA przeciwciała? • Wyizolować pulę limfocytów • Skorzystać z DNA przeciwciała otrzymanego inną metodą • Human Combinatorial Antibody Library (HuCAL) - 7 części zmiennych łańcuchów ciężkich (VH1A, VH1B, VH2-6) i 7 części zmiennych łańcuchów lekkich (Vκ1- Vκ4; Vλ1 – Vλ3) w 49 kombinacjach - Różnorodność przeciwciał wynika ze zmienności w obrębie CDR3, dlatego też CDR3 w tej bibliotece to po prostu przypadkowe trójki nukleotydów - Możliwość otrzymania praktycznie każdego przeciwciała
3 podstawowe problemy w RD: • Białko będąc przyczepionym do kompleksu, musi być jednocześnie prawidłowo zwijane • Łańcuch białka nie może opuścić kompleksu • mRNA nie może opuścić kompleksu 3’ 5’
Rola kodonu STOP • Gdy pojawia się kodon STOP, wtedy kompleks dwóch czynników uwalniających (RF) wiąże się w miejsce tRNA • Uwolnienie białka mRNA w ribosome display nie może posiadać kodonu STOP! Hanes, Pluckthun Proc. Natl. Acad Sci. 94, 4937
Rola ssrA RNA • C-końcowy fragment białka, które powstaje z mRNA bez kodonu STOP, modyfikowany jest przez ssrA RNA (tmRNA) – dodanie „etykietki degradacji” • Uwolnienie białka i degradacja przez specyficzne proteazy W ribosome display ssrA RNA nie może być obecne! Hanes, Pluckthun Proc. Natl. Acad Sci. 94, 4937
mRNA LINKER SD T7 VH VL SMYCZ 5’ stem loop 3’ stem loop Primery SD – PCR 1 Primery T7 – PCR 2 T7 – promotor SD – Shine Dalgarno Linker – bogaty w glicyny i seryny Hanes, Pluckthun Proc. Natl. Acad Sci. 94, 4937
mRNA In vitro transkrypcja DNA In vitro translacja Ekstrakt S30 E.coli lub z retikulocytów królika Reintrodukcja promotora i SD RT PCR 5’ 3’ 5’ 3’ Kompleks stabilizowany wysokim stężeniem Mg++ i niską temperaturą Izolacja mRNA Selekcja mRNA eluowane EDTA 5’ 3’ 3’ 5’ dysocjacja
3 podstawowe problemy zostają rozwiązane: • Białko będąc przyczepionym do kompleksu, musi być jednocześnie prawidłowo zwijane - dodanie izomerazy mostków disiarczkowych - dodanie koktajlu chapperonowego - C-terminalny linker („smycz”) • Łańcuch białka nie może opuścić kompleksu -brak kodonu STOP w mRNA - inhibicja ssrA RNA (oligonukleotydy anty-ssrA) - stabilizacja kompleksu wysokim stężeniem jonów Mg++ • mRNA nie może opuścić kompleksu - brak kodonu STOP - stabilizacja kompleksu wysokim stężeniem jonów Mg++ - inhibitory RNaz - stabilizacja RNA przez struktury stemloop Hanes, Pluckthun Proc. Natl. Acad Sci. 94, 4937
Dlaczego RD jest świetną metodą? • Prowadzona w całości in vitro – możliwość dostosowania warunków reakcji do „indywidualnych potrzeb” białka • Brak transformacji i jej ograniczeń • Możliwość screeningu dużych bibliotek (>1015) • Otrzymanie przeciwciał o bardzo wysokim powinowactwie (1013 M-1) - „dojrzewanie” powinowactwa w każdym cyklu • Bardzo szybkie cykle (produkty pośrednie nie wymagają oczyszczania; otrzymanie białka nie zależy od stanu hodowli komórkowej) • Bardzo czuła • W 5 cyklach RD uzyskano 109krotny wzrost ilości scFv